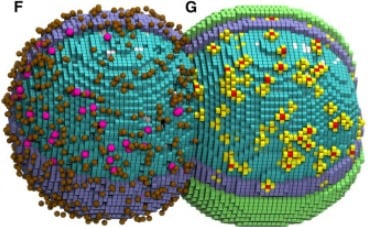
En un laboratorio virtual, una bacteria tan pequeña como un virus se divide con la precisión de un reloj. No es una escena de ciencia ficción, sino el resultado de un experimento que simula de manera digital una célula completa, molécula a molécula, durante todo su ciclo vital.
El avance, liderado por el equipo de Zane R. Thornburg y Andrew Maytin en el J. Craig Venter Institute (JCVI) y la Universidad de Illinois, redefine el alcance de la biología computacional y marca el inicio de una nueva era en el estudio de la vida.
El protagonista de este logro es JCVI-Syn3A, una bacteria con el genoma más simple conocido, compuesta por apenas 493 genes.
Esta célula sintética, diseñada para contener solo los elementos imprescindibles para sobrevivir, sirvió como modelo ideal para un desafío monumental: mapear cada reacción química y cada movimiento físico de todos sus componentes a lo largo de 105 minutos de vida.
La simulación, descrita en la revista Cell, exigió seis días de procesamiento en supercomputadoras para reconstruir un ciclo vital que, en la naturaleza, ocurre en menos de dos horas. “La complejidad de la biología supera con creces nuestra capacidad de procesamiento actual”, reconoció Thornburg.

Un ciclo vital reconstruido molécula a molécula
Para lograr este nivel de detalle, los científicos combinaron modelos matemáticos y simulaciones espaciales cinéticas, utilizando unidades de procesamiento gráfico (GPU) de última generación. Así, pudieron seguir la posición y función de cada ribosoma y cadena de ADN en el interior de la célula, además de reproducir procesos como la replicación del material genético y la síntesis de proteínas.
La simulación 4D —que incorpora el factor tiempo a las tres dimensiones espaciales— permitió observar que, incluso en un organismo mínimo, las reacciones químicas siguen patrones precisos y no se distribuyen al azar. “La organización espacial es el mecanismo crítico que evita el colapso metabólico de la célula, permitiendo que los recursos lleguen a donde se necesitan en el momento preciso de la división”, explicó Thornburg.
Lejos de ser un simple catálogo de genes, la célula digital mostró que la vida depende de una coreografía molecular en la que la ubicación exacta de cada molécula determina el éxito de la división celular.
Los datos revelaron fenómenos imposibles de captar con experimentos tradicionales, como la distribución heterogénea de metabolitos dentro del citoplasma, un dato destacado.
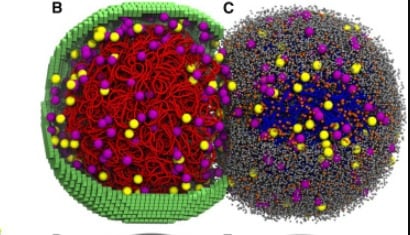
Según la profesora Zaida Luthey-Schulten, coautora del estudio: “La capacidad de capturar con precisión las condiciones en constante cambio dentro de una célula viva abre una nueva ventana a los fundamentos de los sistemas vivos”. La simulación permite anticipar la respuesta de la célula a cientos de experimentos simultáneamente, desde el metabolismo de los nucleótidos hasta la biogénesis de los ribosomas.
El reto computacional detrás de la célula virtual
El trabajo pone de relieve la escala exponencial de la complejidad biológica. Si una célula con menos de 500 genes exige días de supercomputación, simular una célula humana —dotada de unos 20.000 genes— se convierte en un reto de otra dimensión.
El modelo digital también evidenció que cada célula simulada resulta única debido a la variabilidad inherente a los procesos biológicos, una característica que permite comprender mejor la diversidad de comportamientos celulares.
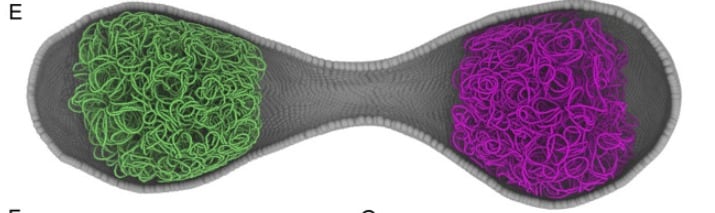
La simulación de la JCVI-Syn3A representa más que un hito técnico. Ofrece una plataforma donde probar, en un entorno seguro, nuevas terapias genéticas y farmacológicas, allanando el camino hacia una medicina personalizada absoluta. “Por primera vez, tenemos un avatar digital que se divide igual que su contraparte biológica”, afirmó Thornburg.
El estudio sugirió que el futuro de la simulación celular estará impulsado por inteligencia artificial, capaz de aprovechar la base de datos generada para predecir la respuesta de las células ante fármacos o mutaciones. Así, la frontera entre la biología y la computación se difumina, permitiendo experimentar en un laboratorio virtual antes de intervenir en organismos vivos.
El proyecto marca “el final de una era y el comienzo de otra”, según sus autores. La capacidad de simular el ciclo vital completo de una célula mínima es el test definitivo para el conocimiento biológico actual y una invitación a descifrar el lenguaje molecular que transforma la materia en vida.